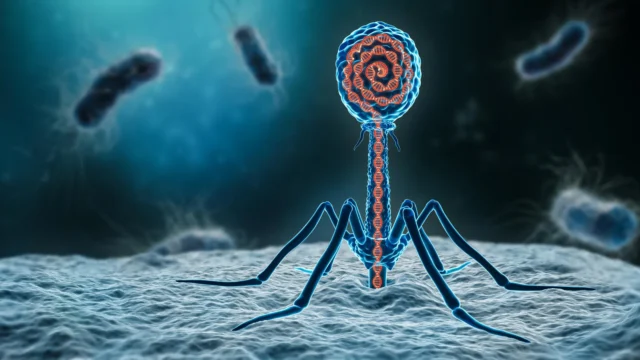
Bacteriófagos são vírus que infectam bactérias e têm sido usados para tratar infecções bacterianas há mais de 100 anos. O interesse nestes vírus está a aumentar novamente à medida que a resistência aos antibióticos se torna uma ameaça crescente à saúde global. Apesar da nova atenção, a maior parte da investigação baseada em fagos continua focada em vírus que ocorrem naturalmente, em grande parte porque os métodos tradicionais de modificação de fagos são lentos, complexos e difíceis de escalar.
em um novo Anais da Academia Nacional de Ciências Neste estudo, cientistas da New England Biolabs (NEB®) e da Universidade de Yale relatam o primeiro sistema totalmente sintético para engenharia de bacteriófagos Pseudomonas aeruginosauma bactéria altamente resistente aos antibióticos e que representa um sério risco em todo o mundo. O método depende da plataforma Golden Gate Assembly (HC-GGA) de alta complexidade do NEB, que permite aos pesquisadores projetar e construir fagos usando dados digitais de sequência de DNA, em vez de depender de amostras virais existentes.
Usando este sistema, a equipe construiu um Pseudomonas aeruginosa Bacteriófago composto por 28 fragmentos de DNA sintético. Eles então programaram o vírus com novas funções, introduzindo mutações pontuais e inserções e deleções de DNA. Essas mudanças permitiram que os pesquisadores trocassem os genes das fibras da cauda para alterar as bactérias que os fagos poderiam infectar e adicionar marcadores fluorescentes para tornar a infecção visível em tempo real.
“Mesmo nas melhores circunstâncias, a engenharia de fagos é extremamente trabalhosa. Os pesquisadores passam toda a sua carreira desenvolvendo processos para projetar fagos modelo específicos em bactérias hospedeiras”, reflete o cientista pesquisador do NEB Andy Sikkema, co-primeiro autor do artigo. “Esta abordagem sintética representa um salto tecnológico em simplicidade, segurança e rapidez, abrindo caminho para a descoberta biológica e o desenvolvimento terapêutico”.
Construindo fagos a partir de DNA digital
Com a plataforma Golden Gate Assembly do NEB, os cientistas podem montar genomas inteiros de fagos fora da célula usando DNA sintético, incorporando todas as alterações genéticas planejadas durante o processo de construção. Uma vez montado, o genoma é introduzido em uma cepa de laboratório segura, onde se torna um fago ativo.
Esta estratégia evita muitos obstáculos de longa data na investigação de fagos. Os métodos tradicionais dependem da manutenção de amostras físicas de fagos e do uso de bactérias hospedeiras especializadas, o que é particularmente desafiador quando se lida com vírus que infectam patógenos humanos perigosos. O novo método também elimina a necessidade de triagem repetida ou edição gradual de genes em células vivas.
Por que a Golden Gate Assembly faz a diferença
Ao contrário de outras tecnologias de montagem de DNA que combinam menos fragmentos, mas mais longos, o Golden Gate Assembly usa fragmentos de DNA mais curtos. Esses fragmentos mais curtos são mais fáceis de produzir, menos tóxicos para as células hospedeiras e menos propensos a conter erros. O método também é adequado para genomas de fagos contendo sequências repetitivas ou conteúdo extremo de GC, ambos os quais muitas vezes complicam a montagem do DNA.
Ao simplificar o processo e expandir as possibilidades técnicas, esta abordagem amplia significativamente o potencial de desenvolvimento de fagos como terapias direcionadas contra infecções resistentes a antibióticos.
A colaboração transforma ferramentas em terapias
O desenvolvimento deste rápido sistema de engenharia de fagos sintéticos resultou de uma estreita colaboração entre cientistas do NEB e pesquisadores de fagos de Yale. Os pesquisadores do NEB passaram vários anos melhorando o Golden Gate Assembly para que ele pudesse lidar de forma confiável com grandes alvos de DNA compostos de muitos fragmentos. Os pesquisadores de Yale reconheceram que essas ferramentas poderiam abrir novas possibilidades na biologia dos fagos e começaram a explorar aplicações mais ambiciosas.
Os cientistas do NEB primeiro otimizaram o método usando vírus modelo bem estudados, E. coli Fago T7. Desde então, a equipe colaborativa expandiu a técnica para fagos não-modelo que têm como alvo algumas das bactérias mais resistentes a antibióticos conhecidas.
Estudos relacionados usando o mesmo método Golden Gate para construir alto conteúdo de GC Micobactérias Phage foi publicado na PNAS em novembro de 2025 em colaboração com o Laboratório Hatfull da Universidade de Pittsburgh e a Ansa Biotechnologies. Em outro exemplo, pesquisadores da Universidade Cornell colaboraram com o NEB para criar fago T7 sinteticamente projetado que serve como biossensor para detectar E. coli As substâncias perigosas na água potável são descritas num estudo da ACS de dezembro de 2025.
“Meu laboratório faz ‘martelos estranhos’ e depois procura o prego certo”, disse Greg Lohman, investigador principal sênior do NEB e coautor do estudo. “Neste caso, a comunidade da terapia fágica nos disse: ‘Este é o martelo que estávamos esperando.'”